发布时间:2025-04-02 17: 16: 00
在分子生物学实验中,PCR扩增的成功与否经常依赖于引物的质量,而引物的稳定性更是直接决定PCR的扩增效率和准确性。我们常用的引物设计软件Oligo,不仅可以用来设计引物序列,还能帮我们快速评估和优化引物的稳定性。那么,今天就来详细讲讲:Oligo怎么评估引物稳定性 怎么用Oligo软件优化引物稳定性,希望能帮大家更高效地完成实验设计。
一、Oligo怎么评估引物稳定性
在用Oligo软件设计好引物序列后,我们并不是马上就可以投入实验,而是需要对引物的稳定性做一个综合评估。这种评估通常包括引物的Tm值(熔解温度)、GC含量、二聚体和发夹结构形成的可能性等等。具体步骤如下:
1、引物序列输入与初步分析
首先,我们打开Oligo软件,在主界面上选择新建文件,然后在引物输入区域输入你设计好的引物序列(一般是20-30个核苷酸)。
输入完成后,Oligo会自动进行初步的序列分析,计算并显示引物的一些基本信息,如长度、GC含量、Tm值和二级结构倾向。
2、评估引物的Tm值
Tm值是PCR实验成功的关键指标之一。一般情况下,我们希望引物的Tm值在55-65℃之间,前后引物Tm值差距不超过2℃。
在Oligo软件中,进入"Analyze"菜单,点击“Melting Temperature”,软件会精确计算引物的Tm值。
我们可以根据结果来决定是否需要调整引物序列。比如Tm值太高或太低都可能导致扩增效率降低或非特异扩增的产生。
3、GC含量与稳定性关系评估
Oligo软件也会自动计算引物的GC含量,一般推荐引物的GC含量控制在40%~60%之间。
GC含量过高会导致Tm值升高,非特异性结合增强;GC含量太低,引物和模板的结合稳定性不足,扩增效果变差。
在Oligo界面的序列分析结果中,我们可以直观看到GC含量指标并进行相应调整。
4、二聚体和发夹结构风险评估
引物的二聚体和发夹结构是严重影响PCR效率的重要因素,Oligo可轻松帮助我们评估这一风险。
点击菜单中的"Analyze" → “Primer Analysis” → “Dimer & Hairpin Structures”,软件会自动计算并预测可能形成的二聚体和发夹结构,并给出风险提示。
一般我们希望看到的是风险较低(如无明显二聚体或发夹结构出现),若提示风险较高,就需要考虑重新设计或优化引物序列。
二、怎么用Oligo软件优化引物稳定性
评估完引物后,如果发现引物稳定性不够理想,Oligo软件提供了一些非常好用的工具,能帮助我们快速进行引物的优化和调整。
1、通过序列微调优化Tm值
假设评估发现引物的Tm值偏低,我们可以尝试增加几个GC碱基;如果Tm值偏高,可以适当减少GC含量或缩短引物长度。
方法很简单,只需要在序列输入窗口中修改引物序列,再次点击“Analyze”→“Melting Temperature”,实时观察Tm值的变化,直到达到理想范围。
2、避免二聚体与发夹结构的优化
如果引物预测容易形成二聚体或发夹结构,这种情况下,可以使用Oligo的自动序列优化功能。
进入菜单,选择“Optimize Primer”或者“Primer Design”→“Avoid Hairpins and Dimers”,软件会自动推荐新的序列组合,有效降低二聚体或发夹结构形成的可能性。
你还可以手动微调碱基,比如适当减少连续重复碱基、降低序列内部互补性,从而减少引物自身配对的风险。
3、使用Oligo内置的引物设计功能自动优化
如果手动调整觉得麻烦,Oligo提供了自动优化功能,只需输入模板序列和所需参数,比如目标产物长度、Tm值范围、GC含量范围、是否避免二聚体等,Oligo会自动设计出最优引物序列。
点击“File”→“Primer Search”,输入模板序列,勾选优化选项,点击搜索按钮。软件会在短时间内给出多个优化好的候选引物序列,你可以从中挑选最理想的一个。
三、引物稳定性优化中的小技巧
除了基本的评估和优化方法,这里再多分享几个能进一步提高引物稳定性的小技巧,帮助你在使用Oligo软件时更加顺手。
1、适当控制引物的长度
通常建议引物长度保持在18-25bp之间,长度适中,既能提供足够稳定的特异性结合,又能避免形成复杂的二级结构。
2、避免连续重复碱基
引物设计中尽量避免连续出现多个相同碱基,比如AAAA或TTTT这样的序列,这种情况极易造成非特异结合或聚合酶滑动,影响扩增效率。
3、注意引物的3’端稳定性
3’端的稳定性对PCR反应的特异性极为关键,建议3’端最后几个碱基最好有1-2个GC碱基,提供更稳定的结合,但又要避免末端过多的GC重复。
4、利用Oligo软件序列对比功能确认特异性
优化完的引物序列,还可以通过Oligo内置的序列比对功能检查其特异性。进入“Analyze”→“Sequence Search”,确认引物序列不会大量匹配到模板上的其他位置,确保扩增产物唯一。
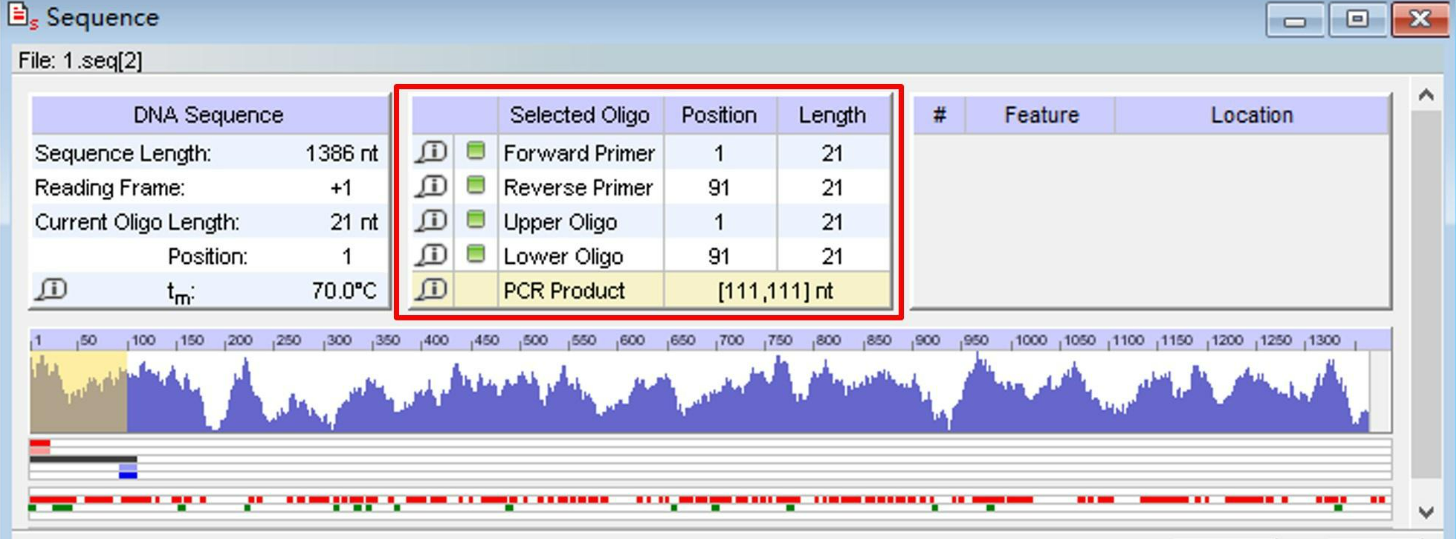
总结
其实,理解了Oligo怎么评估引物稳定性 怎么用Oligo软件优化引物稳定性,我们就可以大大提高PCR实验的成功率,节省大量实验摸索时间。通过掌握Oligo软件提供的评估工具和优化方法,比如Tm值的精确控制、二聚体和发夹结构的规避、自动设计与优化功能的使用等等,你可以更加轻松地设计出稳定、高效的引物。希望今天的这些技巧能帮到你,让你的实验工作更加顺利!
展开阅读全文
︾
读者也喜欢这些内容:
Oligo自定义参数设置灵活吗 Oligo设计参数如何保存模板
在引物设计的专业软件中,Oligo以其高自由度和丰富功能被广泛应用于基因扩增、突变分析、测序等实验场景中。围绕“Oligo自定义参数设置灵活吗,Oligo设计参数如何保存模板”这一主题,本文将详细剖析Oligo的自定义参数体系、模板保存机制以及如何基于既有功能进行流程优化,以帮助科研人员在实际操作中高效使用该软件。...
阅读全文 >

Oligo软件如何分析蛋白质编码序列 Oligo有哪些分析方法?
在分子生物学研究中,蛋白质编码序列的分析对于基因功能注释、表达调控研究至关重要。Oligo软件作为一款经典的生物信息学工具,不仅在引物设计方面表现出色,还在蛋白质编码序列的分析中具有独特优势。那么,Oligo软件如何分析蛋白质编码序列 Oligo有哪些分析方法?下面就为大家详细解读Oligo在蛋白质编码序列分析中的具体应用。...
阅读全文 >
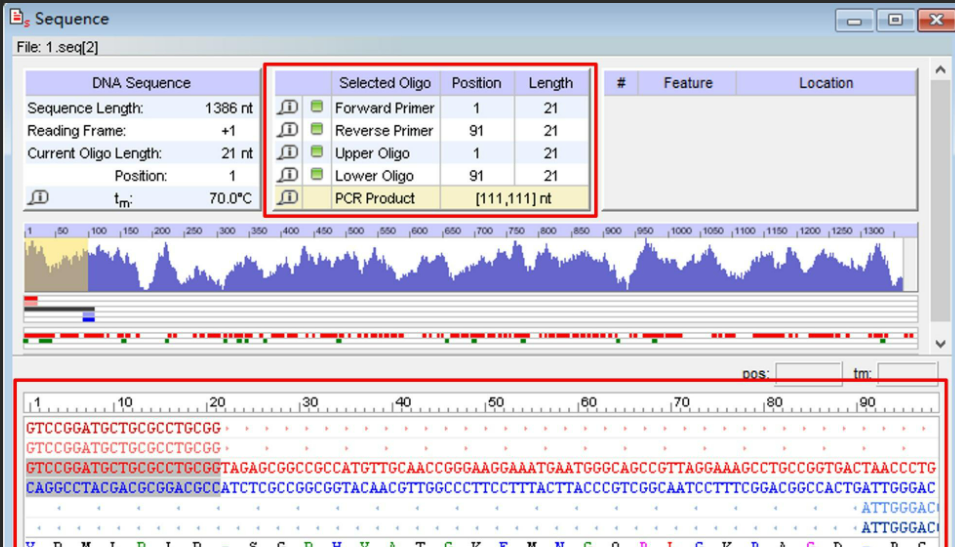
Oligo如何模拟PCR反应 Oligo的PCR反应模拟结果准确吗
在日常分子实验中,PCR(聚合酶链式反应)被广泛应用于基因扩增、突变检测、引物验证等多个核心步骤,而设计合理的引物组合和预测PCR结果的表现,几乎决定了整个实验是否成功。为此,许多科研人员开始依赖专业软件进行模拟预测,其中Oligo软件以其精确的分析能力和详尽的参数设定,在PCR模拟方面表现尤为出色。本文将围绕“Oligo如何模拟PCR反应 Oligo的PCR反应模拟结果准确吗”这一话题,详细解析Oligo在PCR模拟功能上的使用方法、逻辑机制以及结果的可靠性与局限性,帮助你更加科学地规划实验设计。...
阅读全文 >
Oligo软件如何批量设计引物 Oligo批量设计引物有哪些步骤
在分子生物学实验中,引物设计是一项至关重要的基础工作。而在面对多个基因或大批量DNA序列时,手动设计引物不仅耗时费力,还容易出现人为误差。这时,Oligo软件凭借其强大的自动化设计功能,成为很多科研人员的得力助手。本文围绕“Oligo软件如何批量设计引物 Oligo批量设计引物有哪些步骤”这一主题,深入讲解如何高效利用Oligo软件进行批量引物设计,并结合实际应用场景提供详尽的操作指南。...
阅读全文 >