发布时间:2025-01-13 16: 13: 00
在基因扩增实验中,优化引物序列对于提高 PCR 扩增效率、准确性和特异性至关重要。Oligo软件为研究人员提供了强大的引物优化功能,能够根据多种标准调整引物序列,以确保实验结果的可靠性和高效性。本文将介绍Oligo软件如何优化引物序列?引物序列优化的标准是什么。
一、Oligo软件如何优化引物序列?
选择引物设计参数:
在 Oligo 软件中,优化引物序列的第一步是设置正确的引物设计参数。点击 “引物设计”(Primer Design)功能,进入引物设计界面。在这里,用户可以根据实验需求调整以下设计参数:引物长度:常见的引物长度范围为18-25个碱基,太短或太长的引物都可能影响扩增效果。Tm(退火温度):引物的熔解温度(Tm)是设计时的一个关键参数,通常应保持在50-65°C之间,确保引物与模板的结合稳定。GC含量:引物的GC含量应在40%-60%之间,过高或过低的GC含量会导致引物与目标序列结合的效率下降。
引物二聚体和发夹结构:设计引物时要避免引物之间形成二聚体或发夹结构,这样会影响引物的有效性。
自动优化功能:
Oligo软件提供了自动优化功能,通过这些功能,用户可以在软件内设置多个优化目标,例如最大化引物的结合能力、避免二聚体的形成、优化 GC 配比等。软件会自动根据这些参数筛选出最优的引物序列。
验证引物特异性:
Oligo 软件不仅可以帮助用户设计引物,还能通过 BLAST 等工具对引物的特异性进行验证,避免引物在非目标序列中结合,从而提高实验的准确性。
二、引物序列优化的标准是什么?
优化引物序列的标准通常包括以下几个方面:
引物的长度:
理想的引物长度一般为18-25个碱基。过短的引物可能会降低特异性,过长的引物可能会导致非特异性结合。因此,选择合适的长度是优化的首要步骤。
GC含量:
引物的GC含量应当保持在40%-60%之间。GC含量过低可能导致引物与目标序列结合不牢固,而过高的GC含量则可能导致引物自发地形成二级结构或引发非特异性结合。
Tm值(熔解温度):
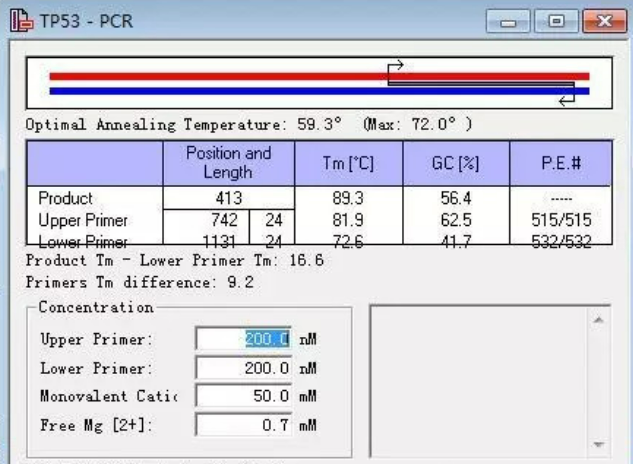
引物的Tm值应当适中,通常控制在50-65°C之间,并且两条引物的Tm差距不宜超过5°C,以确保扩增反应中引物的退火温度适宜。
避免二聚体和发夹结构:
在引物设计过程中,避免引物之间形成二聚体或者发夹结构非常重要。这些结构会导致引物无法有效结合目标序列,从而降低PCR反应的效率。
特异性:
引物应当仅与目标DNA序列结合,避免与基因组中的其他序列结合。使用 BLAST 等在线工具对引物进行特异性检验可以有效避免非特异性扩增。
自定义优化:
Oligo软件允许用户根据实验的实际需求进行灵活的参数设置。对于一些特定的实验,如基因克隆或突变分析,可能会有其他特定的优化标准,如引物的设计周期或突变引导功能。
三、引物优化的常见问题与解决方案
在引物设计和优化的过程中,可能会遇到一些常见的问题。以下是一些问题的解答和解决方案:
引物的效率不高:
如果在 PCR 实验中发现引物效率较低,可能是因为引物的设计参数不合适,特别是 GC含量 或 Tm值。通过调整引物的设计参数,选择合适的引物长度和熔解温度,可以显著提升引物的效率。
非特异性扩增:
非特异性扩增是 PCR 实验中常见的问题,通常是因为引物在非目标序列上产生了结合。解决这一问题的方法是优化引物的特异性,通过 BLAST 或其他工具进行引物的特异性验证,确保引物与目标序列结合。
引物二聚体:
引物二聚体会导致 PCR 扩增失败,产生无效产物。为避免这一问题,Oligo软件能够检测并提示可能的引物二聚体,用户可以根据提示优化引物的序列,减少二聚体的发生。
引物自发形成发夹结构:
引物自发形成发夹结构会影响其与模板DNA的结合效果。通过 Oligo软件的 二级结构分析,可以检测并避免引物形成发夹结构,确保引物的有效性。
总结
以上就是Oligo软件如何优化引物序列?引物序列优化的标准是什么的内容。优化引物序列是确保 PCR 扩增反应成功的关键步骤。通过 Oligo软件,用户可以方便地设计并优化引物序列,确保实验的高效性和准确性。在设计过程中,合理设置引物的长度、GC含量、Tm值等参数,并利用软件的自动优化功能,可以大大提高引物设计的成功率。此外,关注引物的特异性、避免二聚体和发夹结构的形成,也能够进一步提升实验效果。掌握这些引物优化的标准和方法,将有助于研究人员在基因扩增实验中获得更可靠的结果。
展开阅读全文
︾
读者也喜欢这些内容:
Oligo软件如何导出数据到Excel Oligo的导出格式怎么选择
在使用Oligo软件进行引物设计和序列分析时,导出设计结果是一个非常关键的步骤。无论是用于记录、项目归档,还是后续进行实验排版、报告整理,很多用户都希望能将Oligo中的数据直接导出为Excel格式,便于整理和共享。而这就引出了两个核心问题:Oligo软件如何导出数据到Excel,以及Oligo的导出格式怎么选择。本文将从实际操作、格式解析和使用建议等方面,为你详细讲解这一过程。...
阅读全文 >
Oligo软件如何导入外部数据库 Oligo支持哪些数据库
Oligo是一款广泛应用于引物设计、探针筛选及基因合成辅助的专业软件,凭借其高准确性和灵活的功能设置,在分子生物学、基因工程等领域拥有良好的口碑。在实际使用中,很多用户会希望将外部数据库中的序列、注释或物种信息导入Oligo软件中,以便进一步进行高通量的引物筛选或比对分析。那么,Oligo软件如何导入外部数据库Oligo支持哪些数据库,这两个问题也就成了用户经常关注的重点。下面就围绕这两个问题进行详细的讲解。...
阅读全文 >
Oligo怎么评估引物退火温度 Oligo怎么设置引物退火温度
在分子生物学实验中,引物的退火温度(Annealing Temperature,简称Ta)是影响PCR成功与否的关键因素之一。退火温度过高,引物难以与模板结合,可能导致PCR扩增失败;温度过低,则可能产生非特异性扩增。因此,准确评估和设置引物退火温度十分重要。今天,我们就详细聊一聊:Oligo怎么评估引物退火温度 Oligo怎么设置引物退火温度,帮助大家快速掌握使用Oligo软件进行退火温度分析和优化的具体方法。...
阅读全文 >
Oligo怎么评估引物稳定性 怎么用Oligo软件优化引物稳定性
在分子生物学实验中,PCR扩增的成功与否经常依赖于引物的质量,而引物的稳定性更是直接决定PCR的扩增效率和准确性。我们常用的引物设计软件Oligo,不仅可以用来设计引物序列,还能帮我们快速评估和优化引物的稳定性。那么,今天就来详细讲讲:Oligo怎么评估引物稳定性 怎么用Oligo软件优化引物稳定性,希望能帮大家更高效地完成实验设计。...
阅读全文 >