发布时间:2025-06-28 09: 00: 00
在日常的引物设计与分子生物实验中,精准定位特定序列是一项不可或缺的能力。对于使用Oligo软件的科研人员来说,如何快速查找目标DNA或RNA序列,不仅关系到设计效率,更影响到实验的可重复性和科学性。因此,本文将围绕“Oligo软件如何查找特定序列Oligo的查找功能怎么使用”这一主题,深入解析Oligo软件提供的查找功能使用方式及其高效策略。
无论你是刚入门的初学者,还是已经熟悉Oligo使用的科研人员,掌握这些查找技巧都能大大提高工作效率。
一、Oligo软件如何查找特定序列
Oligo软件虽然以引物设计为主,但在处理核酸序列时,也配备了强大的搜索功能。无论是想找出序列中的特定位点、序列片段,还是定位某个剪切位点、重复区域,Oligo都能提供精准匹配。下面介绍具体的查找方法:

1.打开序列文件或项目
启动Oligo软件后,导入或打开你当前需要分析的项目(.oli文件),确保你已加载目标序列信息。如果是一个新的DNA序列,可以通过File→ImportSequence或直接粘贴序列来输入。
2.启用查找工具
点击菜单栏中的:
(1)Edit→FindSequence,或
(2)使用快捷键Ctrl+F(Windows)或Cmd+F(Mac)
将会弹出一个“Find”窗口。
3.输入目标序列片段
在弹出的查找窗口中,输入你要寻找的具体序列,比如"ATGCGT"。此处注意以下设置:
(1)支持大小写匹配(默认不区分)
(2)可选择“匹配正义链”或“反义链”
(3)可以设定匹配的位置范围(例如只在某个区段内找)
4.查看匹配结果
Oligo会高亮显示匹配的序列位置,同时在底部或侧边信息栏标出:
(1)匹配起始位点
(2)是否匹配反义链
(3)所在区域(如引物区域、CDS区域等)
如果有多个匹配,点击“FindNext”可以逐一查看。
5.反向查找/替换序列(高级功能)
对于某些需要进行序列替换的情况(例如替换突变位点),你可以进入Edit→Replace功能,在查找匹配基础上进行替换,但请确保备份项目,以防误操作。
二、Oligo的查找功能怎么使用更高效
Oligo的查找功能并不止步于“查找某段碱基序列”,它实际上可以结合多种参数进行灵活设置,下面介绍一些提高效率的技巧:
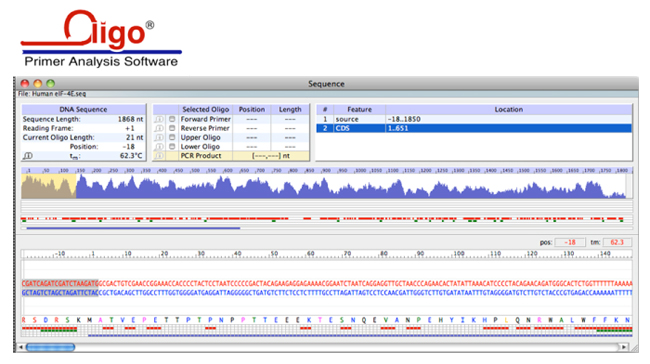
1.查找反义序列
在“FindSequence”窗口中勾选“SearchComplement”,就可以搜索反义链的对应序列片段。这对于PCR引物对称性分析非常有帮助。
2.使用通配符和模糊匹配
某些核酸序列中可能包含变异位点或不确定碱基(如N、R、Y等),Oligo支持部分模糊匹配,可使用IUPAC代码(如W=A/T,R=A/G)进行搜索。
3.限定区域范围查找
在某些情况下,你只想查找特定区域内的序列,比如CDS区、UTR区或某个引物范围。你可以通过设置“范围限制”或在工具栏选择目标区域,然后进行“局部查找”。
4.多序列匹配分析
在设计多个目标时,你可能需要查找一个序列是否出现在多个不同模板中。Oligo支持一次打开多个项目序列,通过“BatchSearch”功能快速筛查。
5.与引物设计功能结合使用
找到目标序列后,可以右键或使用“DesignPrimer”功能,从该位点自动延伸引物设计,减少重复输入的繁琐流程。
6.快速定位保守序列或特征序列
很多功能区如启动子、剪接位点、限制酶识别位点、miRNA结合位点等都有标准化序列,你可以建立自己的“常用序列库”,并利用快捷查找定位到序列中的这些关键片段。
三、如何用查找功能辅助引物设计和验证
查找功能不仅用于分析现有序列,更可以辅助引物设计验证。以下是几个典型应用场景:
1.引物特异性验证
设计好引物后,将引物序列复制到查找框中,搜索整个目标模板,确保该序列只出现一次,避免非特异性扩增。
2.突变验证
通过查找突变碱基(或其前后区域),判断突变是否发生在合适的区域内(如CDS中、关键结构区域等),并为后续测序验证做准备。
3.定位插入序列
在构建表达载体后,查找插入序列是否按预期插入到目标位点,序列拼接是否完整。
4.多样本对比
对于多个来源的模板(如不同物种、不同组织样本),利用查找功能判断序列保守性,是否存在关键差异。
5.跨软件数据验证
Oligo支持导出FASTA、TXT等通用格式,可配合BLAST、SnapGene等工具对比分析。查找功能的准确性,可以作为交叉验证的一部分。
Oligo软件如何查找特定序列Oligo的查找功能怎么使用这个问题,背后实际反映的是科研过程中对效率、准确性和系统性的追求。通过掌握Oligo查找功能的基本操作、进阶设置与实战技巧,科研人员可以在面对复杂序列时迅速定位目标,为后续的引物设计、突变验证、结构分析等任务打下坚实基础。
不论是基础研究中的序列比对,还是应用研发中的结构确认,灵活使用Oligo的查找功能,都是一项提升效率的重要技能。
展开阅读全文
︾
读者也喜欢这些内容:
Oligo发卡结构检测有效吗 Oligo发卡结构如何避免优化
在引物设计与寡核苷酸合成的实践中,发卡结构的形成往往是导致反应失败或效率降低的关键因素。Oligo软件作为一款专业的引物分析与设计工具,其在识别和预测发卡结构方面的功能备受用户关注。围绕Oligo发卡结构检测有效吗,Oligo发卡结构如何避免优化的话题,本文将深入分析Oligo对发卡结构的识别机制、如何有效规避其形成,以及在实际工作中可以进一步扩展的优化建议,帮助科研用户提高实验成功率与设计效率。...
阅读全文 >
反转录过程中常用的引物有哪几类 反转录用随机引物还是olig
在RNA研究与转录组分析中,反转录是基础又关键的一步,它将RNA模板转录成cDNA,为后续PCR扩增、qPCR定量、RNA测序等实验打下基础。实验结果的准确性与反转录使用的引物类型有密切关系。因此,“反转录过程中常用的引物有哪几类,反转录用随机引物还是oligo”成为科研工作者特别关注的问题。本文将围绕这两个核心主题展开详细说明,以提升实验效率与数据质量。...
阅读全文 >
Oligo引物和random引物区别 Oligo dt和随机引物作用一样吗
在分子生物学实验中,逆转录是将RNA转录为cDNA的重要步骤,而引物的选择直接决定了逆转录的效率和特异性。“Oligo引物和random引物区别,Oligodt和随机引物作用一样吗”是实验新手和科研人员经常关注的问题。无论是在qPCR、RNA测序还是文库构建前期,引物选择都会影响到后续分析的可靠性和数据一致性。为了更好地理解这两个引物类型的差异及其在实验中的应用效果,本文将通过三个层面详细分析,并补充扩展一类常见但易被忽视的引物——基因特异性引物。...
阅读全文 >
Oligo软件如何统计序列信息 Oligo怎么导出统计结果
在分子生物学的研究与实验中,对序列的统计分析是一项非常基础却关键的工作。无论是GC含量、碱基组成,还是序列长度与熔解温度(Tm),这些统计信息都直接影响到引物设计、克隆构建、合成策略等各个方面。Oligo软件如何统计序列信息Oligo怎么导出统计结果,成为许多科研人员在实际操作中经常遇到的需求。本文将围绕这个主题,详细介绍Oligo软件中与序列统计相关的核心功能、使用方法和结果导出技巧,帮助用户更高效地获取并利用这些关键数据。...
阅读全文 >